Análisis Factorial Confirmatorio con Indicadores Categóricos
En esta ocasión, realizaremos un análisis factorial confirmatorio con indicadores categóricos.
Iniciamos cargando los paquetes necesarios para el análisis. Los paquetes son: haven para importar datos, lavaan para estimar el Modelo de Ecuaciones Estructurales (SEM), semPlot para crear gráficos de SEM y semTable para producir tablas de SEM.
# Carga paquetes
library(haven) # importar SPSS, Stata, etc.
library(lavaan) # estimar SEM
## This is lavaan 0.6-15
## lavaan is FREE software! Please report any bugs.
library(semPlot) # graficar SEM
library(semTable) # tablas SEM
A continuación, importamos los datos que vamos a analizar. Los datos están almacenados en un archivo .sav de SPSS llamado “ISLCHLC3.sav”. Lo importamos utilizando la función read_spss() del paquete haven.
# Importar datos
#datos <- read_spss("ISLCHLC3.sav")
datos <- read_sav(url("https://github.com/Clases-GabrielSotomayor/pruebapagina/raw/master/content/example/input/data/ISLCHLC3.sav"))
Definimos el modelo de medición para nuestro Análisis Factorial Confirmatorio (AFC). Estamos definiendo un factor latente (“autoritarismo”) y nueve ítems observables. El operador =~ se utiliza para indicar las relaciones entre el factor y los ítems
# Definir modelo de medicion
mod_conf <- 'autoritarismo =~ LS3G01A + LS3G01B + LS3G01C + LS3G01D +
LS3G01E + LS3G01F + LS3G02A + LS3G02B + LS3G02C'
Para ajustar el modelo utilizamos la función cfa() del paquete lavaan. Sin embargo, a diferencia de un análisis factorial confirmatorio con indicadores continuos, debemos especificar que los ítems son categóricos mediante el argumento ordered = T y el estimador utilizado es “DWLS” (Diagonally Weighted Least Squares), que es adecuado para variables categóricas.
# Ajustar modelo CFA
mod_conf_afc <- cfa(mod_conf, data = datos, estimator="DWLS", ordered = T)
Luego, visualizamos un resumen de los resultados del modelo con la función summary(). Activamos las opciones para mostrar las cargas factoriales estandarizadas (standardized = TRUE) e índices de ajuste extendidos (fit.measures = TRUE).
# Resultados
## Salida general
summary(mod_conf_afc,
standardized = TRUE, # mostrar cargas estandarizadas
fit.measures = TRUE) # mostrar índices de ajuste extendidos
## lavaan 0.6.15 ended normally after 19 iterations
##
## Estimator DWLS
## Optimization method NLMINB
## Number of model parameters 36
##
## Used Total
## Number of observations 4864 5081
##
## Model Test User Model:
##
## Test statistic 803.725
## Degrees of freedom 27
## P-value (Chi-square) 0.000
##
## Model Test Baseline Model:
##
## Test statistic 95756.207
## Degrees of freedom 36
## P-value 0.000
##
## User Model versus Baseline Model:
##
## Comparative Fit Index (CFI) 0.992
## Tucker-Lewis Index (TLI) 0.989
##
## Root Mean Square Error of Approximation:
##
## RMSEA 0.077
## 90 Percent confidence interval - lower 0.072
## 90 Percent confidence interval - upper 0.082
## P-value H_0: RMSEA <= 0.050 0.000
## P-value H_0: RMSEA >= 0.080 0.137
##
## Standardized Root Mean Square Residual:
##
## SRMR 0.046
##
## Parameter Estimates:
##
## Standard errors Standard
## Information Expected
## Information saturated (h1) model Unstructured
##
## Latent Variables:
## Estimate Std.Err z-value P(>|z|) Std.lv Std.all
## autoritarismo =~
## LS3G01A 1.000 0.792 0.792
## LS3G01B 1.006 0.010 98.323 0.000 0.797 0.797
## LS3G01C 0.789 0.009 87.222 0.000 0.624 0.624
## LS3G01D 1.018 0.010 100.839 0.000 0.806 0.806
## LS3G01E 0.900 0.009 95.097 0.000 0.713 0.713
## LS3G01F 0.963 0.010 98.674 0.000 0.763 0.763
## LS3G02A 0.877 0.009 93.743 0.000 0.694 0.694
## LS3G02B 1.008 0.010 102.905 0.000 0.798 0.798
## LS3G02C 0.882 0.009 95.410 0.000 0.698 0.698
##
## Intercepts:
## Estimate Std.Err z-value P(>|z|) Std.lv Std.all
## .LS3G01A 0.000 0.000 0.000
## .LS3G01B 0.000 0.000 0.000
## .LS3G01C 0.000 0.000 0.000
## .LS3G01D 0.000 0.000 0.000
## .LS3G01E 0.000 0.000 0.000
## .LS3G01F 0.000 0.000 0.000
## .LS3G02A 0.000 0.000 0.000
## .LS3G02B 0.000 0.000 0.000
## .LS3G02C 0.000 0.000 0.000
## autoritarismo 0.000 0.000 0.000
##
## Thresholds:
## Estimate Std.Err z-value P(>|z|) Std.lv Std.all
## LS3G01A|t1 -1.684 0.031 -54.116 0.000 -1.684 -1.684
## LS3G01A|t2 -1.140 0.023 -49.719 0.000 -1.140 -1.140
## LS3G01A|t3 -0.203 0.018 -11.233 0.000 -0.203 -0.203
## LS3G01B|t1 -1.608 0.030 -54.368 0.000 -1.608 -1.608
## LS3G01B|t2 -0.783 0.020 -38.922 0.000 -0.783 -0.783
## LS3G01B|t3 0.043 0.018 2.409 0.016 0.043 0.043
## LS3G01C|t1 -1.386 0.026 -53.527 0.000 -1.386 -1.386
## LS3G01C|t2 -0.422 0.019 -22.752 0.000 -0.422 -0.422
## LS3G01C|t3 0.586 0.019 30.609 0.000 0.586 0.586
## LS3G01D|t1 -1.702 0.031 -54.023 0.000 -1.702 -1.702
## LS3G01D|t2 -1.076 0.022 -48.210 0.000 -1.076 -1.076
## LS3G01D|t3 -0.072 0.018 -3.985 0.000 -0.072 -0.072
## LS3G01E|t1 -1.125 0.023 -49.373 0.000 -1.125 -1.125
## LS3G01E|t2 -0.346 0.018 -18.829 0.000 -0.346 -0.346
## LS3G01E|t3 0.421 0.019 22.695 0.000 0.421 0.421
## LS3G01F|t1 -1.524 0.028 -54.332 0.000 -1.524 -1.524
## LS3G01F|t2 -0.838 0.020 -40.941 0.000 -0.838 -0.838
## LS3G01F|t3 -0.013 0.018 -0.717 0.473 -0.013 -0.013
## LS3G02A|t1 -1.253 0.024 -51.848 0.000 -1.253 -1.253
## LS3G02A|t2 -0.223 0.018 -12.320 0.000 -0.223 -0.223
## LS3G02A|t3 0.724 0.020 36.571 0.000 0.724 0.724
## LS3G02B|t1 -1.624 0.030 -54.339 0.000 -1.624 -1.624
## LS3G02B|t2 -0.829 0.020 -40.625 0.000 -0.829 -0.829
## LS3G02B|t3 0.175 0.018 9.687 0.000 0.175 0.175
## LS3G02C|t1 -1.357 0.025 -53.236 0.000 -1.357 -1.357
## LS3G02C|t2 -0.435 0.019 -23.376 0.000 -0.435 -0.435
## LS3G02C|t3 0.563 0.019 29.547 0.000 0.563 0.563
##
## Variances:
## Estimate Std.Err z-value P(>|z|) Std.lv Std.all
## .LS3G01A 0.373 0.373 0.373
## .LS3G01B 0.365 0.365 0.365
## .LS3G01C 0.610 0.610 0.610
## .LS3G01D 0.351 0.351 0.351
## .LS3G01E 0.492 0.492 0.492
## .LS3G01F 0.418 0.418 0.418
## .LS3G02A 0.518 0.518 0.518
## .LS3G02B 0.364 0.364 0.364
## .LS3G02C 0.512 0.512 0.512
## autoritarismo 0.627 0.009 73.038 0.000 1.000 1.000
##
## Scales y*:
## Estimate Std.Err z-value P(>|z|) Std.lv Std.all
## LS3G01A 1.000 1.000 1.000
## LS3G01B 1.000 1.000 1.000
## LS3G01C 1.000 1.000 1.000
## LS3G01D 1.000 1.000 1.000
## LS3G01E 1.000 1.000 1.000
## LS3G01F 1.000 1.000 1.000
## LS3G02A 1.000 1.000 1.000
## LS3G02B 1.000 1.000 1.000
## LS3G02C 1.000 1.000 1.000
Además, podemos ver solo los índices de ajuste específicos que nos interesan utilizando la función fitmeasures().
# Ver solo indices de ajuste
fitmeasures(mod_conf_afc,
fit.measures = c("chisq", "df", "pvalue",
"cfi", "rmsea"))
## chisq df pvalue cfi rmsea
## 803.725 27.000 0.000 0.992 0.077
Los índices de ajuste incluyen la chi-cuadrada (chisq), los grados de libertad (df), el p-valor (pvalue), el índice de ajuste comparativo (cfi), y el error cuadrático medio de aproximación (rmsea). Estos índices nos ayudan a evaluar qué tan bien se ajusta el modelo a nuestros datos.
A continuación, creamos un gráfico del modelo usando la función semPaths(). La opción what = “std” se utiliza para mostrar las cargas factoriales estandarizadas en el gráfico.
# Diagrama modelo
semPaths(mod_conf_afc, # modelo ajustado
what = "std", # mostrar cargas estandarizadas
label.cex = 1, edge.label.cex = 1, # tamaño flechas y caracteres
residuals = FALSE, # no mostrar residuos
edge.color = "black") # color flechas
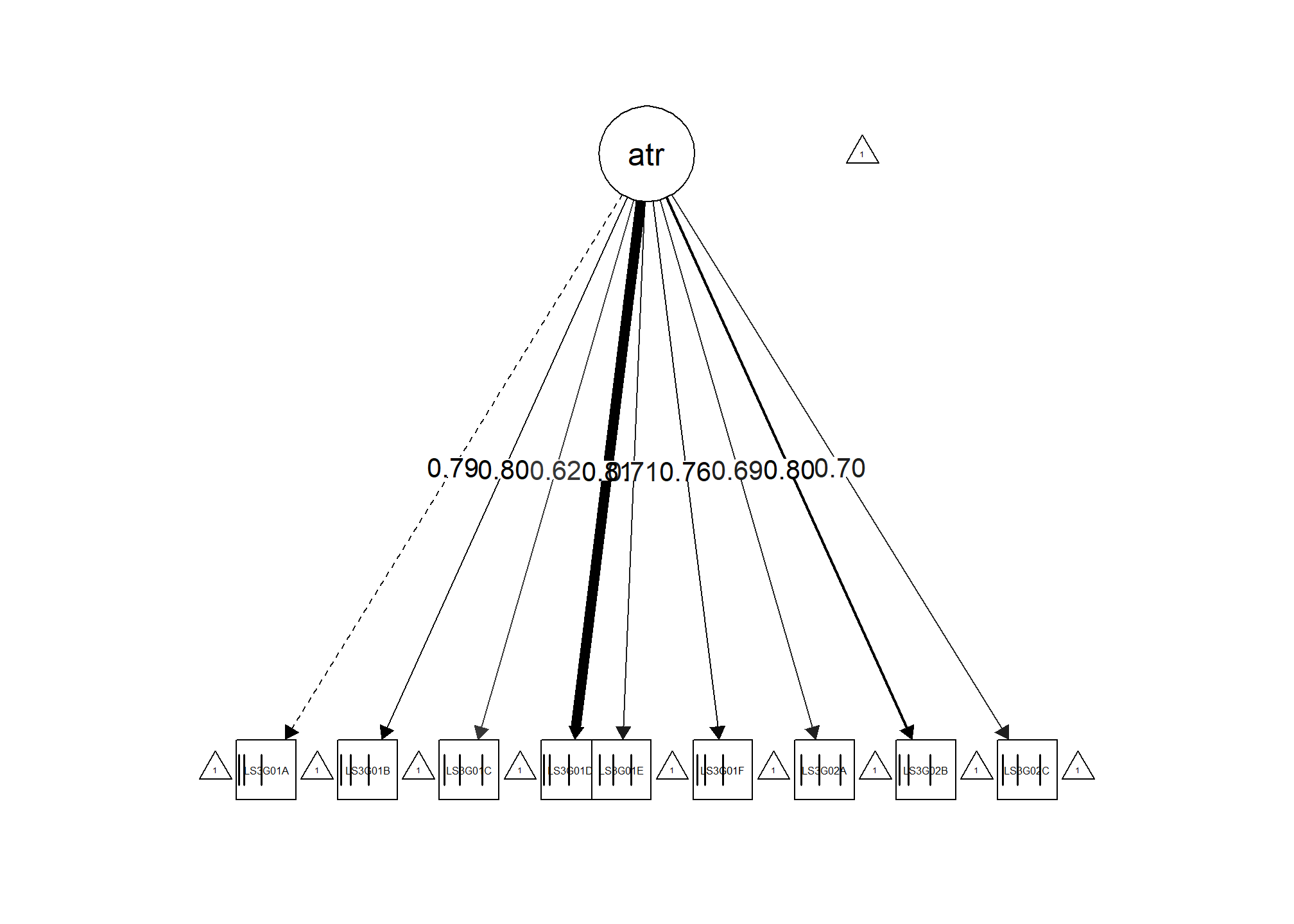 Para interpretar el gráfico, las flechas representan las relaciones entre el factor latente y los ítems. Los números en las flechas son las cargas factoriales estandarizadas, que indican la fuerza de la relación entre cada ítem y el factor.
Para interpretar el gráfico, las flechas representan las relaciones entre el factor latente y los ítems. Los números en las flechas son las cargas factoriales estandarizadas, que indican la fuerza de la relación entre cada ítem y el factor.
A continuación, calculamos las comunalidades, que son las proporciones de varianza de cada ítem que se explican por el factor. Usamos la función inspect() con what = “rsquare” para hacer esto.
# Comunalidades
inspect(mod_conf_afc, what = "rsquare")
## LS3G01A LS3G01B LS3G01C LS3G01D LS3G01E LS3G01F LS3G02A LS3G02B LS3G02C
## 0.627 0.635 0.390 0.649 0.508 0.582 0.482 0.636 0.488
Por último, revisamos los índices de modificación, que sugieren cambios potenciales al modelo que podrían mejorar el ajuste. Mostramos los índices en orden decreciente para identificar los cambios más impactantes primero.
# Indices de modificacion
## Mostrar 'mi' en orden decreciente
modificationindices(mod_conf_afc, sort. = T)
## lhs op rhs mi epc sepc.lv sepc.all sepc.nox
## 101 LS3G02B ~~ LS3G02C 184.051 0.148 0.148 0.343 0.343
## 100 LS3G02A ~~ LS3G02C 120.146 0.125 0.125 0.243 0.243
## 66 LS3G01A ~~ LS3G01B 112.821 0.119 0.119 0.321 0.321
## 99 LS3G02A ~~ LS3G02B 104.847 0.118 0.118 0.272 0.272
## 89 LS3G01D ~~ LS3G02A 61.539 -0.112 -0.112 -0.263 -0.263
## 73 LS3G01A ~~ LS3G02C 58.349 -0.112 -0.112 -0.257 -0.257
## 80 LS3G01B ~~ LS3G02C 56.790 -0.103 -0.103 -0.239 -0.239
## 79 LS3G01B ~~ LS3G02B 46.309 -0.085 -0.085 -0.234 -0.234
## 84 LS3G01C ~~ LS3G02A 37.485 -0.082 -0.082 -0.147 -0.147
## 98 LS3G01F ~~ LS3G02C 34.085 -0.080 -0.080 -0.173 -0.173
## 91 LS3G01D ~~ LS3G02C 32.975 -0.078 -0.078 -0.184 -0.184
## 88 LS3G01D ~~ LS3G01F 31.579 0.065 0.065 0.170 0.170
## 85 LS3G01C ~~ LS3G02B 24.764 -0.067 -0.067 -0.142 -0.142
## 71 LS3G01A ~~ LS3G02A 24.697 -0.073 -0.073 -0.165 -0.165
## 96 LS3G01F ~~ LS3G02A 24.319 -0.069 -0.069 -0.148 -0.148
## 72 LS3G01A ~~ LS3G02B 21.959 -0.060 -0.060 -0.162 -0.162
## 78 LS3G01B ~~ LS3G02A 19.403 -0.059 -0.059 -0.136 -0.136
## 82 LS3G01C ~~ LS3G01E 16.903 0.052 0.052 0.094 0.094
## 81 LS3G01C ~~ LS3G01D 16.692 0.052 0.052 0.113 0.113
## 94 LS3G01E ~~ LS3G02B 11.794 -0.044 -0.044 -0.103 -0.103
## 86 LS3G01C ~~ LS3G02C 11.782 -0.045 -0.045 -0.081 -0.081
## 68 LS3G01A ~~ LS3G01D 10.762 0.039 0.039 0.108 0.108
## 83 LS3G01C ~~ LS3G01F 8.812 0.039 0.039 0.078 0.078
## 97 LS3G01F ~~ LS3G02B 7.148 -0.033 -0.033 -0.085 -0.085
## 74 LS3G01B ~~ LS3G01C 6.864 0.034 0.034 0.071 0.071
## 93 LS3G01E ~~ LS3G02A 6.805 0.033 0.033 0.065 0.065
## 90 LS3G01D ~~ LS3G02B 6.575 -0.030 -0.030 -0.085 -0.085
## 69 LS3G01A ~~ LS3G01E 5.668 -0.033 -0.033 -0.077 -0.077
## 75 LS3G01B ~~ LS3G01D 2.363 0.018 0.018 0.050 0.050
## 77 LS3G01B ~~ LS3G01F 1.290 0.014 0.014 0.035 0.035
## 70 LS3G01A ~~ LS3G01F 0.972 0.012 0.012 0.031 0.031
## 92 LS3G01E ~~ LS3G01F 0.734 0.011 0.011 0.024 0.024
## 87 LS3G01D ~~ LS3G01E 0.597 -0.010 -0.010 -0.024 -0.024
## 67 LS3G01A ~~ LS3G01C 0.349 -0.008 -0.008 -0.018 -0.018
## 95 LS3G01E ~~ LS3G02C 0.092 0.004 0.004 0.008 0.008
## 76 LS3G01B ~~ LS3G01E 0.070 -0.003 -0.003 -0.008 -0.008
Estos índices pueden ayudarte a mejorar tu modelo. Sin embargo, cualquier cambio que hagas en el modelo basándote en estos índices debe tener sentido teórico. No es recomendable hacer cambios al modelo solo porque los índices de modificación sugieran que mejorarán el ajuste.